Specificeer een lineair model om 2 groepen te vergelijken
Om differentieel tot expressie komende genen voor het leukemie-experiment te identificeren, moet je het volgende lineaire model naar R vertalen:
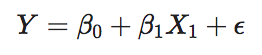
waarbij \(X_{1}\) gelijk is aan 1 voor progressieve kankers en 0 voor stabiele kankers (let op: R kiest automatisch de referentieconditie op basis van alfabetische volgorde).
Deze oefening maakt deel uit van de cursus
Differentiële-expressieanalyse met limma in R
Oefeninstructies
Het ExpressionSet-object eset met de leukemiegegevens is in je werkruimte geladen.
- Gebruik
model.matrixom een designmatrix te maken met een interceptcoëfficiënt en een coëfficiënt die de ziekte-status aangeeft.
Praktische interactieve oefening
Probeer deze oefening eens door deze voorbeeldcode in te vullen.
# Create design matrix for leukemia study
design <- ___(~___, data = ___(eset))
# Count the number of samples modeled by each coefficient
colSums(design)