DGE-theorie: metadata
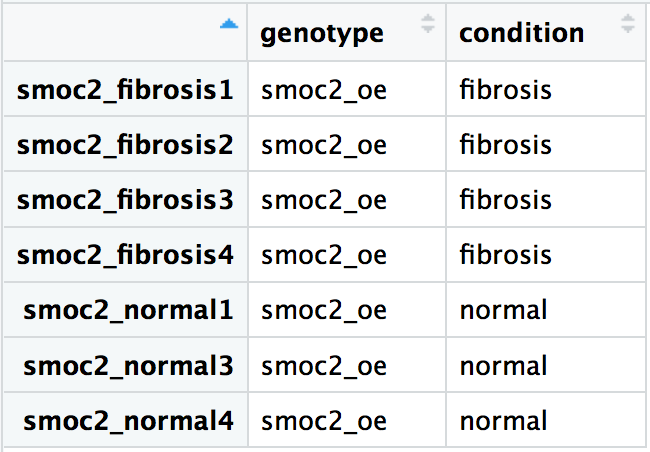
Gebruik de informatie hieronder om een metadata-dataframe te maken voor de fibrose-telgegevens met de naam metadata met kolommen genotype en condition. De samplenames (bijv. smoc2_fibrosis1, smoc2_fibrosis2, enz.) moeten de rijnamen van het dataframe zijn:
Deze oefening maakt deel uit van de cursus
RNA-Seq met Bioconductor in R
Oefeninstructies
- Maak een tekstreeksvector
genotypevoor de bovenstaande gegevens metc(). - Maak een tekstreeksvector
conditionvoor de bovenstaande gegevens metc(). - Maak een dataframe
smoc2_metadatametdata.frame()en de tekstreeksvectorengenotypeencondition. - Maak een vector met samplenames met
c()en wijs die toe aan de rijnamen van het dataframe metrownames().
Praktische interactieve oefening
Probeer deze oefening eens door deze voorbeeldcode in te vullen.
# Create genotype vector
genotype <- c(___)
# Create condition vector
condition <- c(___)
# Create data frame
smoc2_metadata <- data.frame(___, ___)
# Assign the row names of the data frame
rownames(smoc2_metadata) <- c(___)