Het DE-object maken
LET OP: Het kan iets langer duren om deze oefening te laden.
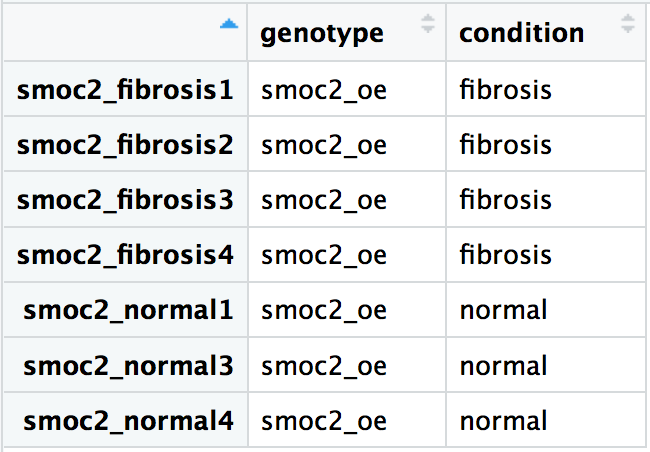
Gebruik onze smoc2-overexpressie-samples om het DESeq2-object te maken, waarbij de ontwerpsformule het verschil in expressie vergelijkt tussen de fibrose- en normale samples. De metadata voor het experiment zie je hieronder. We hebben de data ingelezen met de samples in dezelfde volgorde voor de ruwe smoc2-tellingen, reordered_smoc2_rawcounts, en de metadata, smoc2_metadata.
Deze oefening maakt deel uit van de cursus
RNA-Seq met Bioconductor in R
Oefeninstructies
Maak een DESeq2-object met de naam
dds_smoc2met de functieDESeqDataSetFromMatrix()en geef de argumentencountData,colDataendesignop.Voer de functie
DESeq()uit om de size factors te schatten, de dispersies te berekenen en het model te fitten en te testen.
Praktische interactieve oefening
Probeer deze oefening eens door deze voorbeeldcode in te vullen.
# Create DESeq2 object
dds_smoc2 <- ___(___ = ___,
___ = ___,
___ = ~ condition)
# Run the DESeq2 analysis
___ <- ___(___)