Membuat objek DE
CATATAN: Memuat latihan ini mungkin memerlukan waktu sedikit lebih lama.
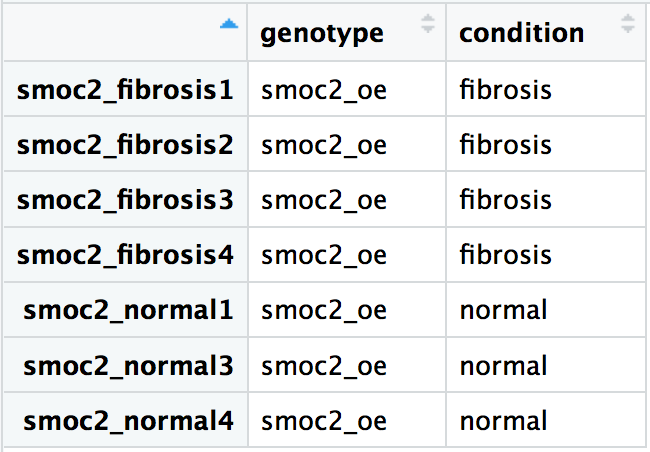
Dengan menggunakan sampel overekspresi smoc2, buat objek DESeq2 sehingga rumus desain menentukan perbandingan perbedaan ekspresi antara sampel fibrosis dan normal. Metadata untuk eksperimen ditampilkan di bawah ini. Data telah dibaca dengan urutan sampel yang sama untuk hitungan mentah smoc2, reordered_smoc2_rawcounts, dan metadata, smoc2_metadata.
Latihan ini adalah bagian dari kursus
RNA-Seq dengan Bioconductor di R
Petunjuk latihan
Buat objek DESeq2 bernama
dds_smoc2menggunakan fungsiDESeqDataSetFromMatrix()dengan menentukan argumen:countData,colData, dandesign.Jalankan fungsi
DESeq()untuk mengestimasi size factors, menghitung dispersi, serta melakukan pemodelan dan pengujian.
Latihan interaktif praktis
Cobalah latihan ini dengan menyelesaikan kode contoh berikut.
# Create DESeq2 object
dds_smoc2 <- ___(___ = ___,
___ = ___,
___ = ~ condition)
# Run the DESeq2 analysis
___ <- ___(___)