Lettere del codice genetico
I mattoni di base dell'RNA sono quattro molecole indicate ciascuna con una singola lettera: adenina (A), citosina (C), guanina (G) e uracile (U). Le informazioni contenute in un filamento di RNA possono essere rappresentate come una lunga sequenza di queste quattro lettere. Per leggere questo codice, bisogna dividere la catena in sequenze di tre lettere ciascuna (ad es. GCU, ACG, …). Queste sequenze di tre lettere sono dette codoni. Il concetto è illustrato nell'immagine qui sotto.
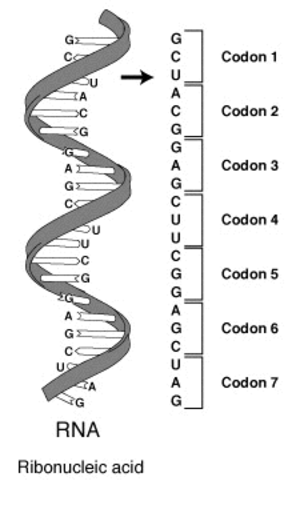
Il tuo obiettivo in questo esercizio è creare un data frame con tutte le possibili sequenze di tre lettere (codoni) a partire da un vettore con le quattro lettere che rappresentano i mattoni dell'RNA.
Questo esercizio fa parte del corso
Rimodellare i dati con tidyr
Esercizio pratico interattivo
Prova a risolvere questo esercizio completando il codice di esempio.
letters <- c("A", "C", "G", "U")
# Create a tibble with all possible 3 way combinations
codon_df <- ___
codon_df